Las unidades de producción, de camarón blanco (L. vannamei) suelen verse afectadas por enfermedades con altas tasas de morbilidad y mortalidad, como el Síndrome de Mancha Blanca. De allí la importancia de estudiar la interacción genotipo por ambiente para peso corporal y supervivencia a cosecha, en presencia y ausencia de este, cuyos resultados sirvan para apoyar los Programas de Mejoramiento Genético.
La producción mundial de camarón blanco del Pacífico (Litopenaeus vannamei) se ha basado en la producción de líneas genéticas que se seleccionan para crecimiento y supervivencia. No obstante, el control del Síndrome de Mancha Blanca (SMB), ha sido una meta difícil de alcanzar y se ha optado por incluir criterios relacionados a la resistencia de esta enfermedad al objetivo de selección de Programas de Mejoramiento Genético (PMG) en peneidos.
“Con esta idea, es importante tener estimadores adecuados de heredabilidad (h2) y correlación genética (rG) para la formulación de estrategias de selección. Estos parámetros genéticos, estimados en condiciones de brote natural, pueden brindar información importante a ser considerada en los PMG.”
En cuanto a la rG para peso y supervivencia en camarón, algunos estudios reportan que no fue posible estimar esta correlación en presencia de SMB, debido a la pérdida de estructura de información derivada de la alta mortalidad en la población.
Además, no existen datos acerca de cómo se modifican estas rG para peso y supervivencia a través de diferentes ambientes en la producción de camarón. Por lo tanto, es importante estimar estos parámetros genéticos (h2 y rG) en presencia o ausencia del SMB para el diseño óptimo de los PMG.
El objetivo de este estudio fue estimar los efectos de la interacción genotipo ambiente (IGA) para peso corporal (PC) y supervivencia a cosecha (SC) en dos ambientes comerciales (presencia o ausencia de brote natural del SMB), en dos líneas genéticas de camarón blanco del Pacífico (L. vannamei), una seleccionada para crecimiento y otra con antecedentes de resistencia al SMB.
MATERIAL Y MÉTODOS
Los datos fueron obtenidos de un laboratorio comercial de producción de larvas de camarón, localizada en el noroeste de México. Los camarones se criaron bajo condiciones comerciales en tres estanques. Se utilizó una línea seleccionada, desde 1998, para crecimiento y supervivencia a cosecha (línea CRE), y otra línea con antecedentes de resistencia a SMB (línea RES). En este estudio, las familias consideradas de cada línea tuvieron un máximo de 25% de genes de la otra línea, y se analizaron de manera independiente.
Origen y desarrollo de las líneas genéticas
La línea CRE fue producida usando camarones provenientes de México, Venezuela, Colombia, Estados Unidos, y Ecuador. La línea RES está compuesta por camarones con antecedentes de resistencia a SMB, procedentes de Ecuador, Panamá y Estados Unidos.
Manejo de familias
Las familias se produjeron mediante inseminación artificial, utilizando una relación de un macho por cada dos hembras para la formación de familias de hembras inseminadas, las cuales desovaron en tanques individuales para el conteo de nauplios por familia (hermanos completos).
Las familias de hermanos completos se mantuvieron en el mismo estanque hasta alrededor de los 60 días de edad, cuando se marcaron.
Manejo de los estanques de crecimiento
Después de diez días del marcaje, se sembraron 36 camarones (en promedio) por familia en cada estanque. La tasa de intercambio diario de agua varió de 5% a 20%. El alimento contó con un porcentaje de proteína entre el 34% y 40%, a razón de 3% de la biomasa total en el estanque. La cantidad de alimentación diaria ofrecida se calculó como el 6% de su biomasa.
Recolección de datos para peso corporal a los 130 días de edad y supervivencia de 70 a 130 días
Para la estimación de la SC, se consideró a los animales recuperados al final del periodo como vivos (1) y los animales no recuperados, tomando la diferencia entre los organismos vivos de cada familia y los sembrados, como muertos (0).
Análisis de la información
El sexo y el estanque también se incluyeron en PC. Los parámetros genéticos para PC y SC se estimaron para cada línea, usando un modelo animal y máxima verosimilitud restringida, con el software ASReml.
Considerando los criterios de aproximación de una distribución binomial a una distribución normal, se asumió normalidad en el análisis de SC.
Las correlaciones genéticas entre ambas características en la combinación línea-estanque se estimaron con ASReml, usando modelos bivariados y con el mismo modelo, pero tomando en cuenta el vector y de información de PC y SC. No se incluyeron restricciones en la estructura de covarianzas y los efectos de ambiente común de familia se consideraron independientes.
“En la estimación de los parámetros genéticos para el PC, los efectos fijos agregados al modelo, fueron: sexo y edad a la cosecha (lineal y cuadrática).”
Adicionalmente, en el caso de SMB-presencia se incorporó el efecto de estanque (Kino y Marea Alta). En cuanto a la SC para los estanques afectados, el único efecto fijo considerado fue el de estanque en SMB-presencia; mientras que en el ambiente SMB-ausencia, no se analizó ningún efecto fijo.
La varianza fenotípica para cada característica, se estimó como la suma de los componentes de varianza de los efectos aleatorios (genético del animal y común de familia), la h2 como la proporción de la varianza fenotípica que se debe a la varianza genética aditiva, y la rG como la covarianza dividida en el producto de las correspondientes desviaciones estándar.
La significancia estadística de los parámetros estimados se basó en los intervalos de confianza (95%), construidos con sus errores estándar, asumiendo normalidad. La existencia de IGA se determinó cuando rG entre ambientes fue menor que 0,80.
Finalmente, para analizar si el comportamiento de las características entre líneas genéticas fue similar, se realizó una comparación de las rG estimadas en cada línea a través de una transformación Z de Fisher
RESULTADOS Y DISCUSIÓN
Comparación del comportamiento productivo entre líneas
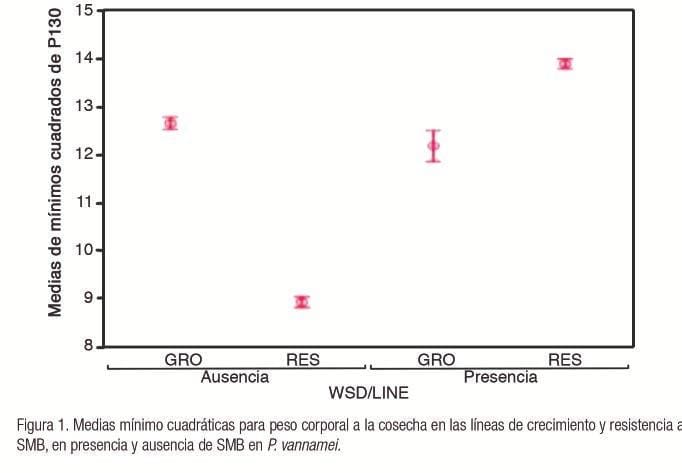
Los resultados muestran diferencias en SC, donde la línea CRE tiene una baja SC en SMB-presencia; mientras que los camarones de la línea RES poseen una menor SC en SMB presencia. Las interacciones de línea por ambiente resaltan la importancia de considerar la probabilidad de ocurrencia de la enfermedad SMB, cuando se elige la línea en el Programa de Mejoramiento Genético (Tabla 1).
Heredabilidades para peso corporal a la cosecha
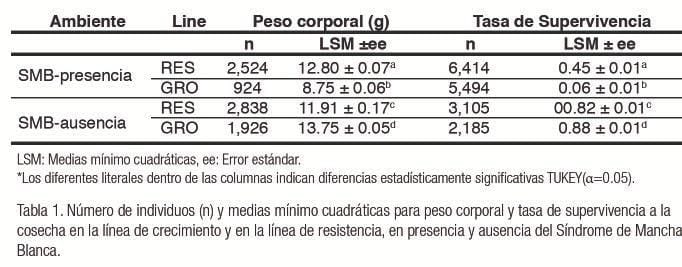
En la línea CRE, la diferencia entre las heredabilidades para SMB-presencia (0,05 ± 0,16) y SMB-ausencia (0,35 ± 0,15), puede ser un indicador de heterogeneidad de varianza; pero en este caso, además de cambios en la varianza genética aditiva, la fuente de esta heterocedasticidad puede estar contenida en cambios en la varianza ambiental por la sensibilidad microambiental de los individuos (Figuras 1 y 2).
Las variaciones en los estimadores de heredabilidad para PC pueden ser resultado de la sensibilidad microambiental de los individuos.
Dado lo anterior, es importante tener en cuenta que estos cambios en la heredabilidad pueden alterar la precisión de la predicción de la respuesta a la selección.
Correlaciones genéticas para PC
No existe efecto de IGA en RES para PC. Considerando que ambas líneas estuvieron en las mismas condiciones ambientales de manejo y expuestas al mismo patógeno (SMB), es posible pensar que las diferencias en los estimadores de ambas líneas son resultado de la baja tasa de SC de la línea CRE.
Heredabilidades para supervivencia a la cosecha en ambas líneas genéticas
Los resultados del modelo de SC fueron consistentes con estimaciones usando modelos univariados, considerando una distribución binomial.
Las heredabilidades en CRE fueron esencialmente cero en ambos ambientes, 0,01 ± 0,02 en SMB presencia y 0,02 ± 0,03 en SMB ausencia, lo cual representa mínimas posibilidades de avance genético por selección para esta característica en ambos escenarios. El avance mínimo por selección podría estar relacionado con la dificultad en la estimación por parte de los modelos estadísticos a causa de la tasa de mortalidad, una proporción genética muy baja en la expresión de la supervivencia o, posiblemente, el daño en la estructura de relaciones genéticas de familia cuando SMB estuvo presente.
Las heredabilidades de SC para ambos ambientes fueron consistentes en ambas líneas, sugiriendo que no existe una compresión de la varianza aditiva en las líneas asociada al ambiente.
“Los resultados de este estudio sugieren que los índices de selección para PC deben tener en cuenta la línea genética usada en el Programa de Mejoramiento Genético.”
La correlación genética entre las dos características no pudo estimarse en SMB-presencia en la línea CRE, probablemente por la afectación en la estructura de la información asociada con la alta mortalidad presente.
En el caso de SMB-ausencia para la línea CRE, la rG no fue diferente de cero, en contraste con la estimada en la línea RES. Las diferencias entre la correlación genética en RES pueden ser indicador de cambios en los componentes de varianza posiblemente asociados a IGA, a su vez relacionada con las covarianzas correspondientes, lo que tendría implicaciones en la respuesta a la selección correlacionada.
“Los resultados de este estudio sugieren que los índices de selección para PC deben tener en cuenta la línea genética usada en el Programa de Mejoramiento Genético.“
Del mismo modo, la estimación de los parámetros genéticos relacionada a PC debe considerar la presencia de enfermedades endémicas, igual que en el caso de SMB en el cultivo de camarón, y visualizar la SC en presencia y ausencia de SMB en calidad de características independientes en ambas líneas genéticas.
Además de los cambios en las heredabilidades y correlaciones genéticas en ambas líneas, su productividad fue diferente en los ambientes estudiados, lo cual podría interpretarse en forma de indicador de plasticidad fenotípica, que puede ser común en organismos marinos y entenderse como la expresión de diferentes fenotipos en individuos con el mismo genotipo, pero bajo diferentes condiciones ambientales.
CONCLUSIONES
Los resultados del modelo lineal sugieren diferencias entre las líneas, tanto para peso corporal como para supervivencia a través de los ambientes; sin embargo, las estimaciones de las correlaciones genéticas no permiten considerar efectos de IGA dentro de línea en ambas características, lo que indicaría que son independientes. Además, las correlaciones genéticas entre las características de la línea de resistencia proponen tratarlas como variables independientes, cuando SMB está presente en el ambiente.

GLOSARIO
Interacción genotipo por ambiente en camarón blanco, Litopenaeus vannamei, asociada a Síndrome de Mancha Blanca
L. vannamei: Litopenaeus vannamei camarón blanco del Pacífico.
SMB: Síndrome de Mancha Blanca.
PMG: Programas de Mejoramiento Genético en peneidos.
h2: Heredabilidad.
rG: Correlación genética.
IGA: Interacción genotipo ambiente.
PC: Peso corporal.
SC: Supervivencia a cosecha.
Línea CRE: Lote de organismos seleccionados por el crecimiento provenientes de México, Venezuela, Colombia, Estados Unidos, y Ecuador.
Línea RES: Lote de organismos seleccionados por la resistencia a SMB procedentes de Ecuador, Panamá y Estados Unidos.

Esta es una versión resumida desarrollada por el equipo editorial de Panorama Acuícola Magazine del artículo “INTERACCIÓN GENOTIPO POR AMBIENTE EN CAMARÓN BLANCO ASOCIADA A SÍNDROME DE MANCHA BLANCA” escrito por CALA-MORENO NELSON, CAMPOS-MONTES GABRIEL, CABALLERO ZAMORA ALEJANDRA, BERRUECOS-VILLALOBOS JOSÉ, CASTILLO-JUÁREZ HECTOR. La versión
original fue publicada en ABRIL de 2021 a través ABANICO VETERINARIO Se puede acceder a la versión completa a través de http://www.scielo.org.mx/scielo.php?pid=S2448-61322021000100111&script=sci_arttext
Más información: Larvas GAM












