Por: Eduardo Martínez-Matus, Cesar Ortega-Santana, Mónica Saldarriaga-Córdoba, Beatriz Cámara y Ruben Avendaño-Herrera*
La tilapia del Nilo (Oreochromis niloticus) es una de las especies más relevantes para la acuicultura mundial, especialmente en América Latina. Su rápida expansión productiva ha favorecido la emergencia y diseminación de enfermedades infecciosas, entre ellas la edwardsiellosis causada por Edwardsiella anguillarum. Este patógeno emergente ha sido recientemente vinculado a eventos de alta mortalidad en diversas especies de peces, posicionándose como una amenaza creciente para la acuicultura.
Introducción
Edwardsiella anguillarum es una bacteria Gram negativa que provoca una enfermedad conocida como edwardsiellosis en peces. Fue descrita originalmente a partir de anguilas (Anguilla japonica) en China (Shao et al., 2015) y, posteriormente, ha sido detectada en diversas especies de peces de importancia comercial. En tilapia, los primeros reportes datan de Estados Unidos en 1997 (Reichley et al., 2017).
Desde entonces, se han documentado brotes de la enfermedad en varios países, incluyendo Costa Rica, Colombia, Corea, Perú, Brasil, Egipto y Taiwán (López- Porras et al., 2018; Armwood et al., 2019; Oh et al., 2020; Sierralta et al., 2020; Da Costa et al., 2022; Elgendy et al., 2022; Rahmawaty et al., 2022). Estos brotes suelen presentarse en condiciones de temperatura cercanas a 29°C y pueden provocar mortalidades variables en campo; sin embargo, en infecciones experimentales se han reportado tasas de mortalidad de hasta el 100% (Oh et al., 2020).
La tilapia del Nilo enfrenta un nuevo desafío sanitario por la diseminación de la edwardsiellosis causada por E. anguillarum. Este patógeno emergente se vincula a eventos de alta mortalidad y signos clínicos como letargia, nado errático y lesiones nodulares en el bazo.
Los peces afectados suelen presentar comportamientos como nado errático y letargia, además de signos clínicos como hemorragias externas y alteraciones internas, incluyendo ascitis y nódulos en órganos como el bazo (López-Porras et al., 2018; Armwood et al., 2019; Elgendy et al., 2022). Dado que estos signos pueden confundirse con otras enfermedades bacterianas granulomatosas, el uso de herramientas moleculares resulta fundamental para la identificación precisa del patógeno (Reichley et al., 2017).
En México, aunque el cultivo de tilapia representa uno de los sectores más importantes de la acuicultura nacional, la presencia de E. anguillarum ha sido escasamente documentada y permanece poco caracterizada. Recientemente, Martínez-Lara et al. (2025) reportaron esta bacteria en tilapia cultivada en el país. En este contexto, y con el fin de aportar nueva evidencia sobre su ocurrencia, el presente estudio tuvo como objetivo confirmar la presencia de este patógeno en tilapia cultivada en dos estados de México mediante el aislamiento y caracterización integral de cuatro aislados bacterianos asociados a brotes de mortalidad, contribuyendo así al fortalecimiento del diagnóstico y la vigilancia sanitaria en la acuicultura de México.

Métodos
El estudio analizó dos brotes infecciosos en tilapia del Nilo (Oreochromis niloticus) ocurridos en México: uno en 2021, en una granja de Querétaro, con mortalidad cercana al 20%, y otro en 2022, en un centro de investigación de la Universidad Autónoma del Estado de México (UAE- Mex) en Toluca, con una mortalidad aproximada del 5%. Los peces afectados presentaron signos clínicos como nado errático, ataxia, distensión abdominal, exoftalmia y alteraciones en la coloración de la piel. Para su diagnóstico, cinco peces de cada brote fueron remitidos al Laboratorio de Sanidad Acuícola del Centro de Investigación y Estudios Avanzados en Salud Animal (CIESA-UAEMex).
Se realizaron necropsias completas, así como raspados de piel y branquias para descartar parásitos externos. Para el aislamiento bacteriano, se tomaron muestras de bazo, hígado y riñón, las cuales fueron sembradas en agar infusión cerebro-corazón (BHI, por sus siglas en inglés) e incubadas a 25°C. Se obtuvieron cuatro aislados bacterianos a partir del bazo de las tilapias, los cuales fueron purificados y conservados a −80°C.
A pesar de la importancia de la tilapia en México, la presencia de E. anguillarum ha sido poco documentada. La identificación precisa requiere herramientas moleculares como la secuenciación de los genes 16SrARN, gyrB y sodB para diferenciarla de otras bacterias granulomatosas.
La identificación molecular preliminar se realizó mediante la secuenciación de los genes 16SrARN, gyrB (Griffin et al., 2014) y sodB (Yamada y Wakabayashi, 1999), los cuales son marcadores validados para la identificación de especies del género Edwardsiella (Reichley et al., 2017). Los análisis filogenéticos se llevaron a cabo utilizando el programa MAFFT (Katoh et al., 2019) y el método Neighbor-Joining (Saitou y Nei, 1987).
La caracterización fenotípica incluyó tinción de Gram, pruebas de movilidad, actividad enzimática y evaluación del crecimiento en diversos medios. Asimismo, se evaluó el crecimiento bajo distintas condiciones de temperatura (0°C – 37°C), salinidad (0% – 6% w/v NaCl) y pH (4 – 10), complementado con sistemas comerciales de identificación bioquímica (API® 20E, API® ZYM y API® 50 CH; BioMérieux).

La susceptibilidad antimicrobiana se evaluó mediante el método de microdilución en caldo, siguiendo las directrices del Clinical and Laboratory Standards Institute (CLSI, 2020), determinando la concentración mínima inhibitoria (CMI) frente a florfenicol, oxitetraciclina, enrofloxacina y eritromicina. La relación genética entre aislados se analizó mediante la amplificación de secuencias palindrómicas repetitivas (REP-PCR) y de secuencias repetitivas intergénicas consenso de enterobacterias (ERIC-PCR), métodos ampliamente utilizados para diferenciación de bacterias Gram negativas (Versalovic et al., 1991; Castro et al., 2011; Reichley et al., 2017).
Además, se secuenció el genoma completo mediante tecnología Illumina. Los genomas fueron sometidos a procesos de control de calidad, ensamblaje, anotación y comparación, mediante análisis de identidad nucleotídica promedio (ANI, por sus siglas en inglés) y filogenómica basada en polimorfismos de nucleótido único (SNP) del genoma central. Asimismo, se investigó la presencia de genes asociados con resistencia antimicrobiana, sistemas de secreción bacteriana y elementos genómicos móviles.
Los aislados mexicanos presentan una alta homogeneidad genética, sugiriendo la dispersión de un linaje clonal entre regiones. El análisis genómico reveló islas de virulencia asociadas a la formación de biofilm y sistemas de secreción, facilitando su adaptación a sistemas de cultivo intensivo.
La patogenicidad se evaluó mediante infección experimental en tilapia. Debido a la alta homogeneidad genética observada entre los aislados, se seleccionó la cepa S-002-23 para el desafío. El aislado fue reactivado mediante pasaje en peces y, posteriormente, se inocularon tilapias sanas con dosis altas (1.3 × 106 UFC/pez) y bajas (3.7 × 104 UFC/ pez) de la bacteria, además de un grupo control. Cada tratamiento incluyó tres réplicas con 10 peces cada una.
Durante un periodo de 14 días, se registraron los signos clínicos y la mortalidad. Los peces muertos fueron examinaron mediante necropsia y, para confirmar la infección, se realizó el aislamiento bacteriano y el análisis histopatológico. Para ello, muestras de hígado, bazo y riñón se fijaron en formalina tamponada al 10% y se procesaron mediante técnicas histológicas convencionales, siguiendo los procedimientos descritos por Ortega et al. (2016).
Resultados
En ambos brotes analizados, las tilapias enfermas presentaron signos clínicos consistentes, incluyendo nado errático, oscurecimiento de la piel, pérdida parcial de escamas y branquias pálidas cubiertas por abundante mucosidad. Durante la necropsia, se observaron de forma recurrente esplenomegalia, hepatomegalia y lesiones nodulares multifocales en hígado y bazo.
Aislamiento bacteriano e identificación molecular
El análisis microbiológico de las muestras del bazo permitió obtener cuatro aislados bacterianos tras 48 – 72 horas en agar BHI a 25°C. Dos aislados se recuperaron del brote ocurrido en Querétaro (S-001-23 y S-002-23) y dos más del brote registrado en el Estado de México (S-003-23 y S-004-23).
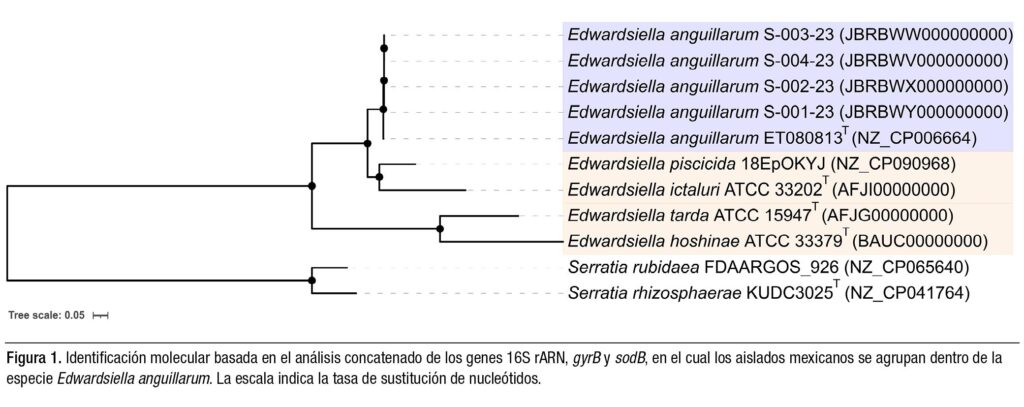
La identificación preliminar mediante la secuenciación de los genes 16SrARN, gyrB y sodB mostró porcentajes de identidad del 99.86%, 99.95% y 100%, respectivamente, con la cepa tipo E. anguillarum ET080813T. El análisis filogenético de las secuencias concatenadas confirmó que los cuatro aislados mexicanos se agrupan dentro del clado de referencia de E. anguillarum ET080813T, con un soporte bootstrap del 100% (Figura 1).
Características fenotípicas y bioquímicas
Todos los aislados presentaron perfiles fenotípicos idénticos, crecieron en todos los medios de cultivo evaluados y no mostraron actividad hemolítica en agar sangre al 5%. Las pruebas bioquímicas revelaron una alta uniformidad entre los aislados. Se observó actividad positiva para glicerol, ornitina descarboxilasa, producción de indol y sulfuro de hidrógeno, así como fermentación de D-manosa, D-manitol, L-arabinosa, maltosa y citrato. Por el contrario, las pruebas de Voges-Proskauer, utilización de trehalosa, Tween 80 y L-fucosa resultaron negativas.
Perfiles de susceptibilidad a antibióticos
Los cuatro aislados bacterianos fueron inhibidos por oxitetraciclina y florfenicol a concentraciones ≤ 1 µg/ mL, indicando una alta susceptibilidad in vitro a estos antibióticos. En contraste, la eritromicina mostró una menor eficacia, con valores de CMI ≤ 64 µg/mL. En el caso de la enrofloxacina, se detectó variabilidad entre los aislados: las cepas S-003-23 y S-004-23 fueron inhibidas a ≤ 0.06 µg/ mL, mientras que S-001-23 y S-002-23 presentaron CMI de ≤ 1 µg/mL.
Tipificación genética
Los análisis de tipificación mediante REP-PCR y ERIC-PCR mostraron patrones idénticos entre los cuatro aislados, lo que sugiere la presencia de un mismo linaje clonal circulante en México, a pesar de que los brotes se registraron en dos estados diferentes del país.
Características genómicas
Los genomas de los cuatro aislados presentaron tamaños muy similares, alrededor de 4.12 Mb, con un contenido de GC cercano al 58.8%, valores consistentes con los reportados para la cepa tipo ET080813T (Shao et al., 2015). El análisis filogenómico basado en más de 16,250 sitios polimórficos confirmó de manera robusta la asignación taxonómica de los aislados mexicanos a E. anguillarum, agrupándose con la cepa tipo con un 100% de soporte estadístico.
Los análisis de ANI mostraron valores superiores al 99.98% entre los aislados, evidenciando una estrecha relación genética y baja diversidad genómica. En comparación con la cepa tipo, la mayoría de las secuencias codificantes se encontraron altamente conservadas, y las diferencias se asociaron principalmente a elementos genéticos móviles, como integrasas, fagos y proteínas hipotéticas.
También se identificaron genes reguladores asociados con resistencia antimicrobiana, como csrA y crp, los cuales estuvieron presentes en todos los genomas analizados. En los aislados S-002-23 y S-004-23 se detectó una variante del gen que codifica el factor de elongación Tu (EF-Tu; tuf), la cual ha sido asociada con la resistencia a las elfamicinas (pulvomicina). El análisis de islas genómicas predijo entre 49 y 77 regiones vinculadas a movilidad genética y factores de virulencia. Asimismo, se identificó un conjunto conservado de genes asociados con la formación de biofilm, incluyendo sistemas de adhesinas, polisacáridos extracelulares, fimbrias y reguladores transcripcionales.
Los aislados muestran susceptibilidad in vitro al florfenicol y oxitetraciclina. Sin embargo, se ha detectado variabilidad en la sensibilidad a la enrofloxacina debido a mutaciones en el gen gyrA, lo que resalta la necesidad de un uso responsable de antibióticos en granjas.
Infección experimental
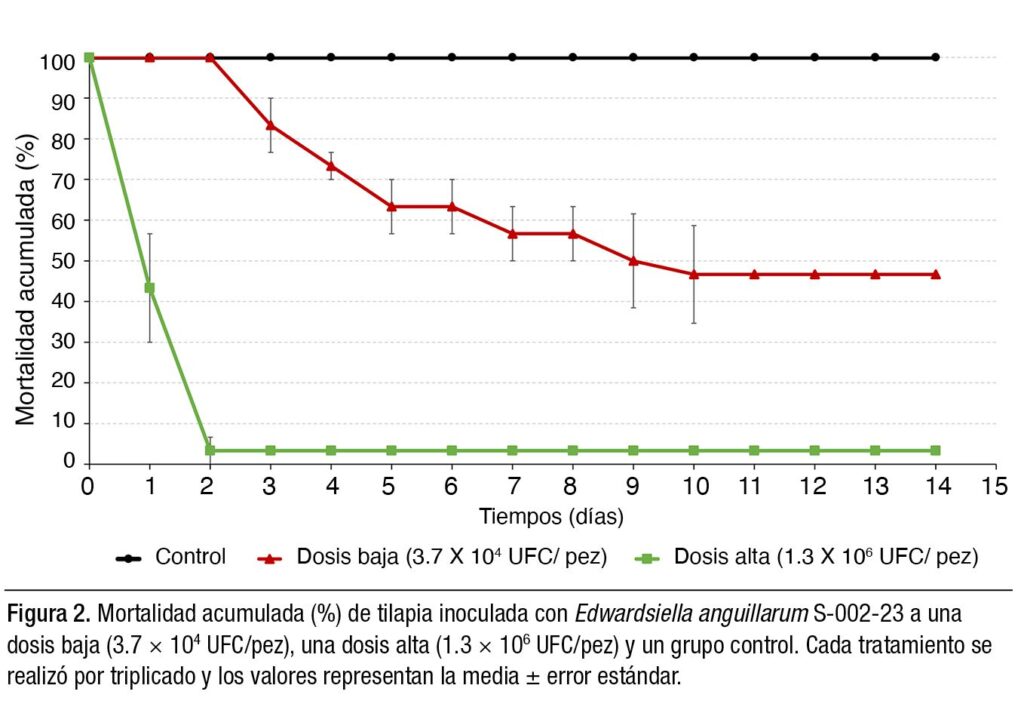
El aislado S-002-23 demostró ser patogénico y altamente virulento en tilapia bajo condiciones experimentales. En el ensayo, se registró una mortalidad acumulada del 97% a la dosis alta (1.3 × 106 UFC/pez) y del 53% a la dosis baja (3.7 × 104 UFC/pez) (Figura 2). En el grupo de dosis alta, el 60% de los peces murió durante las primeras 24 horas, alcanzando una mortalidad del 97% en 48 horas, lo que evidencia una rápida progresión de la infección y un elevado potencial patogénico del aislado.
En el grupo de dosis baja, los peces mostraron alteraciones de comportamiento, como nado en superficie, pérdida del apetito y reducción de la respuesta de escape. También se observaron signos externos como oscurecimiento de la piel, pérdida de escamas y hemorragias en la base del opérculo y en las aletas pectorales. A nivel interno, se detectaron ascitis, hepatomegalia, esplenomegalia y nódulos multifocales en hígado y bazo (Figura 3).

La mortalidad en este grupo se presentó de manera progresiva entre los días 3 y 10 posteriores a la infección. La bacteria se recuperó del cerebro, riñón, hígado y bazo en la mayoría de los peces infectados, confirmando su diseminación sistémica y su papel como agente etiológico. No se registró mortalidad en el grupo control. El análisis histopatológico reveló granulomas en hígado y bazo, acompañados de necrosis celular y hemorragias, lesiones características de la edwardsiellosis.
Discusión
En México, se han identificado previamente bacterias del género Edwardsiella en la microbiota de la trucha arcoíris (Oncorhynchus mykiss) (Salgado-Miranda et al., 2010) y en ambientes marinos mediante análisis metagenómicos (Escobedo-Hinojosa y Pardo-López, 2017). Sin embargo, los reportes en tilapia han sido limitados, y recientemente E. anguillarum fue detectada en tilapia cultivada en el estado de Jalisco (Martínez-Lara et al., 2025).
En este estudio, la identificación preliminar de E. anguillarum se sustentó en el análisis de los genes gyrB y sodB junto con la caracterización bioquímica de los aislados, lo que permitió una diferenciación robusta respecto a otras especies del género, como E. piscicida y E. ictaluri. Aunque los perfiles bioquímicos fueron consistentes con la especie, se observaron variaciones menores respecto a la cepa tipo ET080813T, lo que refleja la variabilidad fenotípica intraespecífica previamente descrita (Shao et al., 2015; Elgendy et al., 2022). Asimismo, todos los aislados carecieron de actividad hemolítica, coincidiendo con reportes previos para esta especie (Ucko et al., 2016).
Infecciones experimentales confirman que E. anguillarum es altamente virulenta, alcanzando mortalidades acumuladas de hasta el 97% en solo 48 horas. El patógeno causa diseminación sistémica, afectando hígado, bazo y riñón, comprometiendo gravemente la viabilidad económica de la producción acuícola.
En cuanto a la susceptibilidad antimicrobiana, todos los aislados mostraron susceptibilidad al florfenicol y a la oxitetraciclina, mientras que la eritromicina presentó menor actividad inhibitoria. Dos aislados (S-001-23 y S-002-23) también mostraron menor susceptibilidad a la enrofloxacina, lo cual se asoció con la mutación S83R en el gen gyrA, previamente relacionada con resistencia a las quinolonas en E. tarda (Shin et al., 2005).

Los análisis de tipificación genética y genómica revelaron una alta similitud entre los cuatro aislados, evidenciando la presencia de un linaje clonal, a pesar de su distinto origen geográfico. Este hallazgo sugiere la posible dispersión del patógeno entre regiones a través del movimiento de peces entre granjas y centros de producción, una práctica común en la acuicultura intensiva. De hecho, los peces involucrados en los brotes estudiados provenían de criaderos ubicados en los estados de Veracruz e Hidalgo, lo que respalda la hipótesis de una distribución más amplia de E. anguillarum en México de lo previamente reconocido (Martínez-Lara et al., 2025).
El análisis genómico confirmó un alto porcentaje de identidad nucleotídica entre los aislados y la cepa tipo, además de la presencia de un número considerable de islas genómicas potenciales asociadas con elementos móviles y factores de virulencia. Estos resultados reflejan la plasticidad genómica de la especie, lo que podría facilitar su adaptación a distintos ambientes y hospederos (Shao et al., 2015; Byadgi et al., 2022; Katharios et al., 2019).
Los ensayos de infección experimental confirmaron el potencial patogénico del aislado S-002-23, que provocó elevadas tasas de mortalidad en tilapia. La virulencia observada fue superior a la reportada en otros aislados previamente descritos, como SGLFS1 de México (Martínez-Lara et al., 2025), SNU2 de Corea (Oh et al., 2020) y OT109003-14 y EA_110.E51 de Taiwán (Rahmawaty et al., 2022, 2024).
Finalmente, los peces infectados desarrollaron lesiones características de la edwardsiellosis, como hemorragias cutáneas, ascitis y granulomas en hígado y bazo, confirmando la consistencia clínica de la infección. Lesiones similares han sido descritas en brotes de E. anguillarum en tilapia en Costa Rica y Egipto (López-Porras et al., 2018; Armwood et al., 2019; Elgendy et al., 2022). Además, estudios recientes han documentado infiltración inflamatoria en el intestino de peces infectados, lo que podría explicar la acumulación de líquido intestinal observada en este estudio (Rahmawaty et al., 2024).
Conclusión
En la presente investigación se confirma E. anguillarum como un patógeno bacteriano responsable de brotes infecciosos en granjas de tilapia en México, aportando nueva evidencia sobre su presencia, distribución y capacidad patogénica en el país. Este agente fue capaz de provocar mortalidades de hasta el 97% en condiciones experimentales, lo que evidencia su impacto potencial en la producción. En conjunto, estos hallazgos amplían el conocimiento epidemiológico de esta bacteria y subrayan la necesidad de fortalecer las estrategias de vigilancia y bioseguridad para mitigar su riesgo en la acuicultura nacional.
Versión resumida del artículo “ISOLATION AND COMPREHENSIVE CHARACTERISATION OF EDWARDSIELLA ANGUILLARUM FROM DISEASED TILAPIA (Oreochromis niloticus) CULTURED IN MEXICO: BIOCHEMICAL,GENETIC AND GENOMIC INSIGHTS AND DOSE-DEPENDENT PATHOGENICITY” escrito por MARTÍNEZ-MATUS, E.– Universidad Andrés Bello, Interdisciplinary Center for Aquaculture Research –INCAR2 & Universidad Técnica Federico Santa María; ORTEGA-SANTANA, C.– Universidad Autónoma del Estado de México; SALDARRIAGA-CÓRDOBA, M.– Universidad Bernardo O’Higgins; CÁMARA,B.– Universidad Técnica Federico Santa María; AVENDAÑO-HERRERA, R.–Universidad Andrés Bello & Interdisciplinary Center for Aquaculture Research –INCAR2. Este trabajo fue financiado por la Agencia Nacional de Investigación e Innovación mediante los proyectos ANID INCAR2 CIA250009 y ANID Becas Doctorado Nacional 21232432. El artículo, que incluye tablas y figuras, fue publicado el 18 de febrero de 2026 en JOURNAL OF FISH DISEASES. La versión completa está disponible en https://doi.org/10.1111/ jfd.70147
* Eduardo Martínez-Matus1,2,3, Cesar Ortega-Santana4, Mónica Saldarriaga- Córdoba2,5, Beatriz Cámara3 y Ruben Avendaño-Herrera1,2,6
1 Laboratorio de Patología de Organismos Acuáticos y Biotecnología Acuícola, Facultad de Ciencias de la Vida, Universidad Andrés Bello, Viña del Mar, Chile.
2 Centro FONDAP, Interdisciplinary Center for Aquaculture Research –INCAR2, Universidad Andrés Bello, Viña del Mar, Chile.
3 Actino Lab USM, Centro de Biotecnología “Daniel Alkalay Lowitt” y Departamento de Química, Universidad Técnica Federico Santa María, Valparaíso, Chile.
4 Centro de Investigación y Estudios Avanzados en Salud Animal, Facultad de Medicina Veterinaria y Zootecnia, Universidad Autónoma del Estado de México, Toluca, México.
5 Escuela de Medicina Veterinaria, Centro de Investigación en Recursos Naturales y Sustentabilidad, Universidad Bernardo O’Higgins, Santiago, Chile.
6 Centro de Investigación Marina Quintay (CIMARQ), Universidad Andrés Bello, Quintay, Chile.













